| 번호 | 청구항 |
|---|---|
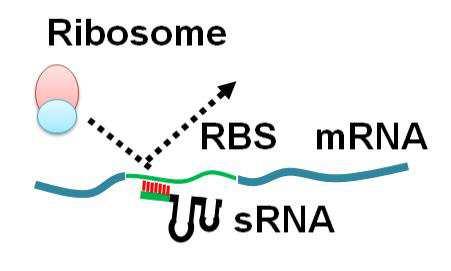
| 1 | 원핵생물에서 유전자 발현을 억제하는 sRNA에 있어서, 다음을 포함하는 것을 특징으로 하는 합성 sRNA:(i) MicC, SgrS 및 MicF 중 어느 하나의 sRNA 유래의 Hfq 결합 부위(Hfq binding site) 및 (ii) 표적 유전자 mRNA와 상보적 결합을 형성하는 영역여기서, 상기 (i)의 Hfq 결합 부위가 MicC 유래인 경우, 상기 (ii)의 표적유전자는 OmpC가 아니고, 상기 (i)의 Hfq 결합 부위가 SgrS 유래인 경우, 상기 (ii)의 표적유전자는 PtsG가 아니며, 상기 (i)의 Hfq 결합 부위가 MicF 유래인 경우, 상기 (ii)의 표적유전자는 OmpF가 아님,여기서, 상기 Hfq 결합 부위는 서열번호 140의 1 |
| 2 | 제1항에 있어서, 상기 표적 유전자 mRNA와 상보적 결합을 형성하는 영역은 표적 유전자 mRNA의 리보좀 결합 부위 (Ribosome binding site)와 전체적으로 또는 부분적으로 상보적 결합을 형성하는 것을 특징으로 하는 sRNA. |
| 3 | 제1항에 있어서, 상기 표적 유전자 mRNA와 상보적 결합을 형성하는 영역 중 하나 이상의 뉴클레오티드를 결실시키거나 치환하여 표적 유전자의 mRNA와 결합하지 않는 부위를 형성시킨 것을 특징으로 하는 sRNA. |
| 4 | 제1항에 있어서, 상기 표적 유전자 mRNA와 상보적 결합을 형성하는 영역에 하나 이상의 뉴클레오티드를 삽입하여 표적 유전자의 mRNA와 결합하지 않는 부위를 형성시킨 것을 특징으로 하는 sRNA. |
| 5 | 제1항에 있어서, 상기 표적 유전자 mRNA와 상보적 결합을 형성하는 영역은, 상기 표적 유전자 mRNA와의 결합에너지가 -10kcal/mol 내지 -40kcal/mol이 되도록 구성하는 것을 특징으로 하는 sRNA. |
| 6 | 제5항에 있어서, 상기 표적 유전자 mRNA와 상보적 결합을 형성하는 영역은, 상기 표적 유전자 mRNA와의 결합에너지가 -20kcal/mol 내지 -40kcal/mol이 되도록 구성하는 것을 특징으로 하는 sRNA. |
| 7 | 제1항에 있어서, MicC 유래의 Hfq 결합 부위를 포함하고 있는 것을 특징으로 하는 sRNA. |
| 8 | 제1항에 있어서, 상기 원핵생물은 대장균, 리조비움(Rhizobium), 비피도박테리움 (Bifidobacterium), 로도코커스 (Rhodococcus), 칸디다 (Candida), 에르위니아(Erwinia), 엔테로박터 (Enterobacter), 파스테렐라(Pasteurella), 멘하이미아 (Mannheimia), 액티노바실러스 (Actinobacillus), 아그레가티박터 (Aggregatibacter), 잔토모나스(Xanthomonas), 비브리오(Vibrio), 슈도모나스(Pseudomonas), 아조토박터(Azotobacter), 애시네토박터(Acinetobacter), 랄스토니아(Ralstonia), 아그로박테리움(Agrobacterium), 리조비움(Rhizobium), 로도박터(Rhodobacter), 자이모모나스(Zymomonas), 바실러스(Bacillus), 스테필로코커스(Staphylococcus), 락토코커스(Lactococcus), 스트렙토코커스(Streptococcus), 락토바실러스(Lactobacillus), 클로스트리디움(Clostridium), 코리네박테리움(Corynebacterium), 스트렙토마이세스(Streptomyces), 비피도박테리움(Bifidobacterium) 및 사이클로박테리움(Cyclobacterium)로 구성되는 군에서 선택된 것임을 특징으로 하는 sRNA. |
| 9 | 제1항에 있어서, 상기 표적 mRNA는 DsRed2, LuxR, AraC, KanR (kanamycin resistance gene), tyrR(tyrosine regulator), ppc (phosphoenolpyruvate carboxylase), csrA (carbon storage regulator), pgi (glucose-6-phosphate isomerase), glt (citrate synthase), accA (acetyl-CoA carboxyltransferase, alpha-subunit), accB (biotinylated biotin-carboxyl carrier protein), accC (acetyl-CoA carboxylase), accD (acetyl-CoA carboxyltransferase, beta-subunit), aceE (subunit of E1p component of pyruvate dehydrogenase complex), aceF (pyruvate dehydrogenase), ackA (propionate kinase / acetate kinase activity), adiY (AdiY is a positive DNA-binding transcriptional regulator that controls the arginine) decarboxylase (adi) system), argB (acetylglutamate kinase), argC (N-acetylglutamylphosphate reductase), argG (argininosuccinate synthase), argH (argininosuccinate lyase), asnC (transcriptional regulator that activates the expression of asnA, a gene involved in the synthesis of asparagine), aspA (aspartate ammonia-lyase), crp (CRP transcriptional dual regulator), csiD (predicted protein. CsiD is the product of a gene induced by carbon starvation), csiR (DNA-binding transcriptional repressor), cytR (transcription factor required for transport and utilization of ribonucleosides and deoxyribonucleosides), dcuA (The DcuA transporter is one of three transporters known to be responsible for the uptake of C4-dicarboxylates such as fumarate under anaerobic conditions), deoB (phosphopentomutase), deoC (deoxyribose-phosphate aldolase), deoR (The transcriptional repressor DeoR, for "Deoxyribose Regulator," is involved in the negative expression of genes related to transport and catabolism of deoxyribonucleoside nucleotides), fabH (KASIII, -ketoacyl-ACP synthases), fadD (fatty acyl-CoA synthetase), fadR (FadR Fatty acid degradation Regulon, is a multifunctional dual regulator that exerts negative control over the fatty acid degradative regulon [Simons80, Simons80a] and acetate metabolism), fbp (fructose-1,6-bisphosphatase), fnr (FNR is the primary transcriptional regulator that mediates the transition from aerobic to anaerobic growth), fruR (FruR is a dual transcriptional regulator that plays a pleiotropic role to modulate the direction of carbon flow through the different metabolic pathways of energy metabolism, but independently of the CRP regulator) , ftsL (essential cell division protein FtsL), ftsQ (essential cell division protein FtsQ), ftsW (essential cell division protein FtsW), ftsZ (essential cell division protein FtsZ), fur (Fur-Fe+2 DNA-binding transcriptional dual regulator), gabD (succinate semialdehyde dehydrogenase, NADP+-dependent), gabP (APC transporter), gabT (4-aminobutyrate aminotransferase), gadA (glutamate decarboxylase A subunit), gadB (glutamate decarboxylase B subunit), gadC (GABA APC transporter), glcC (GntR family transcriptional regulator, glc operon transcriptional activator), glpK (glycerol kinase), glpR (sn-Glycerol-3-phosphate repressor), glpX (fructose 1,6-bisphosphatase II), gltA (citrate synthase), hfld (lysogenization regulator), ihfa (IHF, Integration host factor, is a global regulatory protein), ihfb (IHF, Integration host factor, is a global regulatory protein), ilvB (acetohydroxybutanoate synthase / acetolactate synthase), ilvC (acetohydroxy acid isomeroreductase), ilvD (dihydroxy acid dehydratase), ilvG_1 (acetolactate synthase II, large subunit, N-ter fragment (pseudogene)), ilvG_2 (acetolactate synthase II, large subunit, C-ter fragment (pseudogene)), ilvH (acetolactate synthase / acetohydroxybutanoate synthase), ilvL (ilvGEDA operon leader peptide), ilvM (acetohydroxybutanoate synthase / acetolactate synthase), ilvN (acetohydroxybutanoate synthase / acetolactate synthase), ilvX (Predicted small protein), lexA (LexA represses the transcription of several genes involved in the cellular response to DNA damage), lpxC (UDP-3-O-acyl-N-acetylglucosamine deacetylase), marA (MarA participates in controlling several genes involved in resistance to antibiotics, oxidative stress, organic solvents and heavy metals.), metJ (MetJ transcriptional repressor), modE (ModE is the principal regulator that controls the transcription of operons involved in the transport of molybdenum and synthesis of molybdoenzymes and molybdate-related functions), nadB (L-aspartate oxidase), narL (nitrate/nitrite response regulator), pck (phosphoenolpyruvate carboxykinase), PdhR (PdhR, "pyruvate dehydrogenase complex regulator," regulates genes involved in the pyruvate dehydrogenase complex), phoP (PhoP-Phosphorylated DNA-binding transcriptional dual regulator. Member of the two-component regulatory system phoQ/phoP involved in adaptation to low Mg2+ environments and the control of acid resistance genes), pnuC (PnuC NMN transporter), ppsA (phosphoenolpyruvate synthetase), pta (Phosphate acetyltransferase), purA (adenylosuccinate synthetase), purB (adenylosuccinate lyase), purR (PurR-Hypoxanthine DNA-binding transcriptional repressor. PurR dimer controls several genes involved in purine nucleotide biosynthesis and its own synthesis), puuE (4-aminobutyrate aminotransferase), rbsA (ribose ABC transporter), rbsB (ribose ABC transporter), rbsD (ribose pyranase), rbsK (ribokinase), rbsR (The transcription factor RbsR, for "Ribose Repressor," is negatively autoregulated and controls the transcription of the operon involved in ribose catabolism and transport), rcsB (RcsB-BglJ DNA-binding transcriptional activator. RcsB protein for "Regulator capsule synthesis B," is a response regulator that belongs to the multicomponent RcsF/RcsC/RcsD/RcsA-RcsB phosphorelay system and is involved in the regulation of the synthesis of colanic acid capsule, cell division, periplasmic proteins, motility, and a small RNA) , rutR (RutR regulates genes directly or indirectly involved in the complex pathway of pyrimidine metabolism), serA (alpha-ketoglutarate reductase / D-3-phosphoglycerate dehydrogenase), serC (phosphohydroxythreonine aminotransferase / 3-phosphoserine aminotransferase), soxS (dual transcriptional activator and participates in the removal of superoxide and nitric oxide), sroD (SroD small RNA), zwf (glucose 6-phosphate-1-dehydrogenase), asnA (asparagine synthetase A), asnB (asparagine synthetase B), carA (carbamoyl phosphate synthetase), carB (carbamoyl phosphate synthetase), ddlB (D-alanine-D-alanine ligase B), deoA (thymidine phosphorylase / uracil phosphorylase), deoD (purine nucleoside phosphorylase deoD-type), dpiA (dual transcriptional regulator involved in anaerobic citrate catabolism), fis (Fis, "factor for inversion stimulation", is a small DNA-binding and bending protein whose main role appears to be the organization and maintenance of nucleoid structure), gadE (GadE controls the transcription of genes involved in glutamate dependent system), gadW (GadW controls the transcription of genes involved in glutamate dependent system), gadX (GadX controls the transcription of genes involved in glutamate dependent system), glpF (GlpF glycerol MIP channel), ilvY (IlvY DNA-binding transcriptional dual regulator), ivbL (The ilvB operon leader peptide (IvbL)), lhgO (L-2-hydroxyglutarate oxidase), lpd (Lipoamide dehydrogenase), lrp (Lrp is a dual transcriptional regulator for at least 10% of the genes in Escherichia coli. These genes are involved in amino acid biosynthesis and catabolism, nutrient transport, pili synthesis, and other cellular functions, including 1-carbon metabolism), metB (O-succinylhomoserine lyase / O-succinylhomoserine(thiol)-lyase), metL (aspartate kinase / homoserine dehydrogenase), mraY (phospho-N-acetylmuramoyl-pentapeptide transferase), mraZ (Unknown function), murE (UDP-N-acetylmuramoylalanyl-D-glutamate 2,6-diaminopimelate ligase), murF (D-alanyl-D-alanine-adding enzyme), murG (N-acetylglucosaminyl transferase), nac (Nacregulates, without a coeffector, genes involved in nitrogen metabolism under nitrogen-limiting conditions), nadA (quinolinate synthase), nsrR (NsrR, the "nitrite-sensitive repressor" regulates genes involved in cell protection against nitric oxide (NO) ), panC (pantothenate synthetase), panD (Aspartate 1-decarboxylase), pgl (6-phosphogluconolactonase), pyrB (aspartate carbamoyltransferase, PyrB subunit), pyrC (dihydroorotase), pyrL (aspartate carbamoyltransferase, PyrI subunit), rob (Rob is a transcriptional dual regulator. Its N-terminal domain shares 49% identity with MarA and SoxS. These proteins activate a common set of about 50 target genes, the marA/soxS/rob regulon, involved in antibiotic resistance, superoxide resistance, and tolerance to organic solvents and heavy metals.) , rpe (ribulose phosphate 3-epimerase), talA (transaldolase A), thrA (aspartate kinase / homoserine dehydrogenase), thrB (homoserine kinase), thrC (threonine synthase), thrL (thr operon leader peptide), tktA (transketolase I), tktB (transketolase II) 및 torR (two-component system, OmpR family, torCAD operon response regulator TorR)로 구성되는 군에서 선택된 유전자의 mRNA인 것을 특징으로 하는 sRNA. |
| 10 | 제1항 내지 제9항 중 어느 한 항의 sRNA를 코딩(encoding)하는 분리된 핵산. |
| 11 | 제1항 내지 제9항 중 어느 한 항의 sRNA를 코딩(encoding)하는 분리된 핵산을 포함하는 발현벡터. |
| 12 | 제1항 내지 제9항 중 어느 한 항의 sRNA가 도입된 재조합 미생물. |
| 13 | 제11항의 발현벡터로 형질전환된 재조합 미생물. |
| 14 | MicC, SgrS 및 MicF 중 어느 하나의 sRNA 유래의 Hfq 결합 부위(Hfq binding site)를 코딩하는 핵산에 표적 유전자 mRNA와 상보적 결합을 형성하는 영역을 코딩하는 핵산을 연결하는 단계를 포함하는 sRNA의 제조방법:여기서, 상기 Hfq 결합 부위가 MicC 유래인 경우, 상기 표적유전자는 OmpC가 아니고, 상기 Hfq 결합 부위가 SgrS 유래인 경우, 상기 표적유전자는 PtsG가 아니며, 상기 Hfq 결합 부위가 MicF 유래인 경우, 상기 표적유전자는 OmpF가 아님,여기서, 상기 Hfq 결합 부위는 서열번호 140의 1 |
| 15 | 제14항에 있어서, MicC, SgrS 및 MicF 중 어느 하나의 sRNA의 mRNA 결합 서열을 제거하고 상기 표적 유전자 mRNA와 상보적 결합을 형성하는 영역을 코딩하는 핵산을 도입하는 것을 특징으로 하는 방법. |
| 16 | 제14항에 있어서, 상기 표적 유전자 mRNA와 상보적 결합을 형성하는 영역은 표적 유전자 mRNA의 리보좀 결합 부위 (Ribosome binding site)와 전체적으로 또는 부분적으로 상보적 결합을 형성하는 것을 특징으로 하는 방법. |
| 17 | 제14항에 있어서, 상기 표적 유전자 mRNA와 상보적 결합을 형성하는 영역을 코딩하는 핵산 상의 하나 이상의 뉴클레오티드를 결실시키거나 치환하여 표적 유전자의 mRNA와 결합하지 않는 부위를 형성시키는 것을 특징으로 하는 방법. |
| 18 | 제14항에 있어서, 상기 표적 유전자 mRNA와 상보적 결합을 형성하는 영역을 코딩하는 핵산에 하나 이상의 뉴클레오티드를 삽입하여 표적 유전자의 mRNA와 결합하지 않는 부위를 형성시킨 것을 특징으로 하는 방법. |
| 19 | 제14항에 있어서, 상기 표적 유전자 mRNA와 상보적 결합을 형성하는 영역은, 상기 표적 유전자 mRNA와의 결합에너지가 -10kcal/mol 내지 -40kcal/mol이 되도록 구성하는 것을 특징으로 하는 방법. |
| 20 | 제19항에 있어서, 상기 표적 유전자 mRNA와 상보적 결합을 형성하는 영역은, 상기 표적 유전자 mRNA와의 결합에너지가 -20kcal/mol 내지 -40kcal/mol이 되도록 구성하는 것을 특징으로 하는 방법. |
| 21 | 제1항 내지 제9항 중 어느 한 항의 sRNA를 원핵생물 내로 도입하거나 원핵생물 내에서 발현시키는 단계; 및 표적 유전자의 mRNA 발현을 억제하는 단계를 포함하는 표적 유전자의 발현 억제 방법. |
| 22 | 제21항에 있어서, 상기 sRNA의 발현은 유도물질(inducer) 결합에 따라 작동하는 프로모터에 의하여 이루어지는 것을 특징으로 하는 방법. |
| 23 | 제21항에 있어서, 상기 sRNA의 발현은 온도 민감성 전사 조절 단백질(temperature-senstive transcription factor)에 의하여 억제되는 것을 특징으로 하는 것을 특징으로 하는 방법. |
| 24 | 제1항 내지 제9항 중 어느 한 항의 sRNA를 포함하는 원핵생물에서 표적 유전자 발현 억제용 조성물. |
| 25 | 다음 단계를 포함하는 유용물질 생산을 위한 결실대상 유전자의 스크리닝 방법:(a) 유용물질을 생산하고자 하는 대상 균주에 존재하고, 유용물질 생합성 경로에 참여하는 유전자들 중 어느 하나 이상의 유전자를 제1항 내지 제9항 중 어느 한 항의 sRNA의 표적 유전자로 하여 발현을 억제시키는 단계; 및(b) 상기 발현 억제에 따라 유용물질 생산수율이 향상되는 경우, 발현을 억제시킨 유전자를 유용물질 생산을 위한 결실대상 유전자로 선정하는 단계. |
| 26 | 다음 단계를 포함하는 유용물질 생산균주의 개량방법:(a) 유용물질을 생산하고자 하는 대상 균주에 존재하고, 유용물질 생합성 경로에 참여하는 유전자들 중 어느 하나 이상의 유전자를 제1항 내지 제9항 중 어느 한 항의 sRNA의 표적 유전자로 하여 발현을 억제시키는 단계; (b) 상기 발현 억제에 따라 유용물질 생산수율이 향상되는 경우, 발현을 억제시킨 유전자를 유용물질 생산을 위한 결실대상 유전자로 스크리닝하는 단계; 및(c) 상기 스크리닝된 유전자 또는 스크리닝된 유전자의 조합을 결실시킨 재조합 균주를 제조하는 단계. |
| 27 | 타이로신(Tyrosine) 생합성 경로를 가지는 숙주세포에 MicC, SgrS 및 MicF 중 어느 하나의 sRNA 유래의 Hfq 결합 부위(Hfq binding site) 및 tyrR 또는 csrA 유전자의 mRNA와 상보적 결합을 형성하는 영역을 포함하는 것을 특징으로 하는 합성 sRNA가 도입되거나 발현됨으로써 tyrR 및 csrA 유전자의 발현을 억제하여 tyrR 및 csrA 유전자의 기능이 상실된 것을 특징으로 하는 타이로신 생산능력이 향상된 재조합 미생물;여기서, 상기 Hfq 결합 부위는 서열번호 140의 1 |
| 28 | 삭제 |
| 29 | 제27항에 있어서, ppsA (phenolpthiocerol synthesis type-I polyketide synthase A), tktA (transketolase), aroG/aroF (3-deoxy-7-phosphoheptulonate synthase), aroK (shikimate kinase I) 및 tyrC (prephenate dehydrogenase)로 구성되는 군에서 선택된 하나 이상의 유전자가 도입 또는 증폭되어 있는 것을 특징으로 하는 재조합 미생물. |
| 30 | 삭제 |
| 31 | 제27항에 있어서, 상기 숙주세포는 대장균, 리조비움(Rhizobium), 비피도박테리움 (Bifidobacterium), 로도코커스 (Rhodococcus), 칸디다 (Candida), 에르위니아(Erwinia), 엔테로박터 (Enterobacter), 파스테렐라(Pasteurella), 멘하이미아 (Mannheimia), 액티노바실러스 (Actinobacillus), 아그레가티박터 (Aggregatibacter), 잔토모나스(Xanthomonas), 비브리오(Vibrio), 슈도모나스(Pseudomonas), 아조토박터(Azotobacter), 애시네토박터(Acinetobacter), 랄스토니아(Ralstonia), 아그로박테리움(Agrobacterium), 리조비움(Rhizobium), 로도박터(Rhodobacter), 자이모모나스(Zymomonas), 바실러스(Bacillus), 스테필로코커스(Staphylococcus), 락토코커스(Lactococcus), 스트렙토코커스(Streptococcus), 락토바실러스(Lactobacillus), 클로스트리디움(Clostridium), 코리네박테리움(Corynebacterium), 스트렙토마이세스(Streptomyces), 비피도박테리움(Bifidobacterium) 및 사이클로박테리움(Cyclobacterium)로 구성되는 군에서 선택된 것임을 특징으로 하는 재조합 미생물. |
| 32 | 제31항에 있어서, E.coli S17-1 (ATCC 47055)인 것을 특징으로 하는 재조합 미생물. |
| 33 | 제27항의 재조합 미생물에 tpl 유전자를 도입하거나 증폭시킨 것을 특징으로 하는 페놀 생산능을 가지는 재조합 미생물. |
| 34 | 제33항에 있어서, E.coli W3110 (ATCC 39936)인 것을 특징으로 하는 재조합 미생물. |
| 35 | 타이로신(Tyrosine) 생합성 경로를 가지는 숙주세포에 MicC, SgrS 및 MicF 중 어느 하나의 sRNA 유래의 Hfq 결합 부위(Hfq binding site) 및 tyrR 또는 csrA 유전자의 mRNA와 상보적 결합을 형성하는 영역을 포함하는 것을 특징으로 하는 합성 sRNA를 도입시키거나 발현시킴으로써 tyrR 및 csrA 유전자의 발현을 억제하여 tyrR 및 csrA 유전자의 기능이 상실시키는 것을 포함하는 타이로신 생산능력이 향상된 재조합 미생물의 제조방법;여기서, 상기 Hfq 결합 부위는 서열번호 140의 1 |
| 36 | 삭제 |
| 37 | 카다베린(Cadaverine) 생합성 경로를 가지는 숙주세포에 MicC, SgrS 및 MicF 중 어느 하나의 sRNA 유래의 Hfq 결합 부위(Hfq binding site) 및 murE, metB, thrL 및 ackA로 구성되는 군에서 선택된 어느 하나 이상의 유전자의 mRNA와 상보적 결합을 형성하는 영역을 포함하는 것을 특징으로 하는 합성 sRNA가 도입되거나 발현됨으로써 murE, metB, thrL 및 ackA로 구성되는 군에서 선택된 어느 하나 이상의 유전자의 발현을 억제하여 murE, metB, thrL 및 ackA로 구성되는 군에서 선택된 어느 하나 이상의 유전자의 기능이 상실된 것을 특징으로 하는 카다베린 생산능력이 향상된 재조합 미생물;여기서, 상기 Hfq 결합 부위는 서열번호 140의 1 |
| 38 | 삭제 |
| 39 | 삭제 |
| 40 | 제37항에 있어서, 상기 숙주세포는 대장균, 리조비움(Rhizobium), 비피도박테리움 (Bifidobacterium), 로도코커스 (Rhodococcus), 칸디다 (Candida), 에르위니아(Erwinia), 엔테로박터 (Enterobacter), 파스테렐라(Pasteurella), 멘하이미아 (Mannheimia), 액티노바실러스 (Actinobacillus), 아그레가티박터 (Aggregatibacter), 잔토모나스(Xanthomonas), 비브리오(Vibrio), 슈도모나스(Pseudomonas), 아조토박터(Azotobacter), 애시네토박터(Acinetobacter), 랄스토니아(Ralstonia), 아그로박테리움(Agrobacterium), 리조비움(Rhizobium), 로도박터(Rhodobacter), 자이모모나스(Zymomonas), 바실러스(Bacillus), 스테필로코커스(Staphylococcus), 락토코커스(Lactococcus), 스트렙토코커스(Streptococcus), 락토바실러스(Lactobacillus), 클로스트리디움(Clostridium), 코리네박테리움(Corynebacterium), 스트렙토마이세스(Streptomyces), 비피도박테리움(Bifidobacterium) 및 사이클로박테리움(Cyclobacterium)로 구성되는 군에서 선택된 것임을 특징으로 하는 재조합 미생물. |
| 41 | 카다베린(Cadaverine) 생합성 경로를 가지는 숙주세포에 MicC, SgrS 및 MicF 중 어느 하나의 sRNA 유래의 Hfq 결합 부위(Hfq binding site) 및 murE, metB, thrL 및 ackA로 구성되는 군에서 선택된 어느 하나 이상의 유전자의 mRNA와 상보적 결합을 형성하는 영역을 포함하는 것을 특징으로 하는 합성 sRNA를 도입시키거나 발현시킴으로써 murE, metB, thrL 및 ackA로 구성되는 군에서 선택된 어느 하나 이상의 유전자의 발현을 억제하여 murE, metB, thrL 및 ackA로 구성되는 군에서 선택된 어느 하나 이상의 유전자의 기능이 상실시키는 단계를 포함하는 카다베린 생산능력이 향상된 재조합 미생물의 제조방법;여기서, 상기 Hfq 결합 부위는 서열번호 140의 1 |
| 42 | 삭제 |
| 43 | 삭제 |